RCaller 无法返回复杂数据的研究以及解决方案
2017-09-22 15:41
423 查看
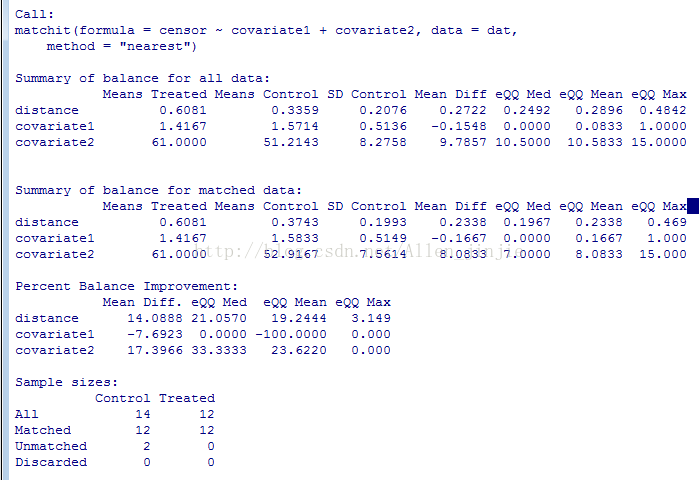
在 Java调用基于 R 的 One-Way ANOVA检测 文章里,通过 cbind 我们可以返回多个数据,但是里面的数据都是简单类型,所有能正常工作,但是我在做 Propensity Score Match 的时候调用 MatchIt 函数,我需要将分析结果数据全部返回,下面是数据在 RGui
里面的样子:
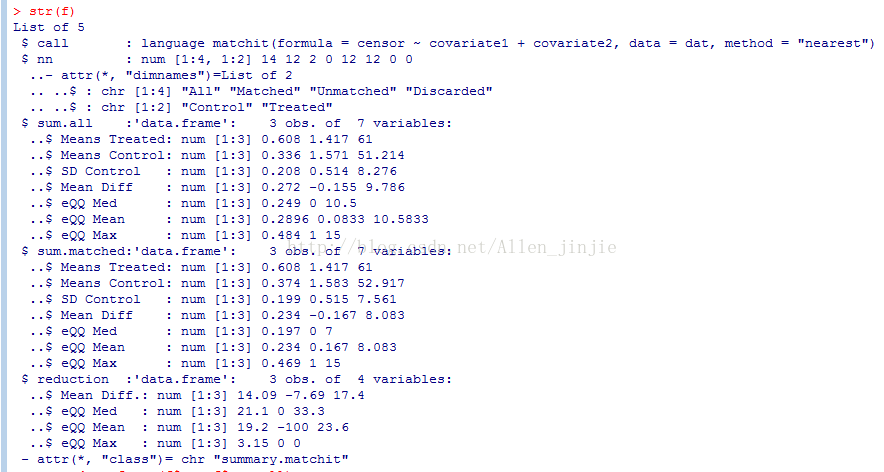
获取各个 Matrix 的函数:
我的程序是这样的:
程序运行时,RCaller 报 Rcaller Error in strsplit(names, "\\.") 错误,逐行注释调试,如果直接获取 sa , 报
1. RCaller 把R代码写入文件中,调用Rscript执行;
2. 执行之后RCaller通过试图把R结果转成xml格式,返回给Java;我们的R代码没有问题,问题出在转xml的部分;
3. RCaller转xml的时候,它默认每个数据(包括list),每一列都要有名字,而我们java代码里边的out变量,没有名字,所以objnames<-names(obj)为空,导致运行出错;
尝试着给每个列都取名字, 把Java代码写成这样:
又会遇到 RCaller 的第二个问题,数据类型支持不全:
因为 sa, mat 的类型都是 list,而 ss 是其支持的类型,不然根本进入不了 if 语句里,原样返回了xmlcode而已,所以Java里只能看到ss,调用获取别的都出错。
所以,对于复杂的类型返回,就不要使用 RCaller, 但是 RCaller 的 API 友好性真的不错,如果分析的结果比较简单,还是喜欢使用这个工具。
=================更新 @ 2017/09/26=====================
既然 RCaller 支持的类型比较有限,那么为了返回结果能够进入这些 if 语句块,我们是不是可以对结果数据进行转型,比如 mat 是一个 list 类型,我们是否有办法将其转型为 vector, 这样不就可以了。google 了下,发现了 Better way to convert list
to vector? 里面提到了 unlist(myList, use.names=FALSE)将转型和对 out 里面的每个返回值赋予一个名字,终于出结果了。但是发现了另外一个问题,具体描述见 difference between as.data.frame and read.csv in
R
其实,真正写程序的时候,是页面传变量的ID/Name, 后台查询数据库得出值,因为不知道变量返回值的类型,我统一使用 String 接收,然后放入 RCaller 的 RCode里,生成 R 的完整程序里,可以看到每个变量的值都是字符串。把程序抓出来放到 RGui 里面,打印data.frame并不能看出其类型,但是可以通过 sapply 函数得知:
> sapply(df, class)
PERSON_ID OUTCOME tnb gxy AGE1
"factor" "factor" "factor" "factor" "factor"由于是 factor 类型,表示是离散值,非数字, matchit 不会把他们当数字处理,只罗列所有离散值。
解决办法有两个,一个就是在输入 RCode 之前,就将变量值转成数字型。另一个就是在 R 执行 matchit 之前,对 data.frame 的列进行转型:
newdf = transform( df, tnb = as.numeric( tnb ), AGE1=as.numeric( AGE1 ) )
sapply( newdf, class )
PERSON_ID OUTCOME tnb gxy AGE1
"factor" "factor" "numeric" "factor" "numeric"
最终,我采取了在传入 RCode 之前,就对数据转型成数字,然后传入 RCode。首先我的 R 程序的生成文件在 C:\Users\Lenovo\AppData\Local\Temp 路径下 (Lenovo是我的机器名),完整代码如下:
cleanNames<-function(names){
cln<-paste(unlist(strsplit(names,"\\.")),collapse="_")
cln<-paste(unlist(strsplit(cln,"<")),collapse="")
cln<-paste(unlist(strsplit(cln,">")),collapse="")
cln<-paste(unlist(strsplit(cln," ")),collapse="")
cln<-paste(unlist(strsplit(cln,"\\(")),collapse="")
cln<-paste(unlist(strsplit(cln,"\\)")),collapse="")
cln<-paste(unlist(strsplit(cln,"\\[")),collapse="")
cln<-paste(unlist(strsplit(cln,"\\]")),collapse="")
cln<-paste(unlist(strsplit(cln,"\\*")),collapse="")
cln<-paste(unlist(strsplit(cln,"&")),collapse="")
return(cln)
}
replaceXMLchars <- function(aStr){
cln <-paste(unlist(strsplit(aStr,"&")),collapse="&")
cln <-paste(unlist(strsplit(cln,"<")),collapse="<")
cln <-paste(unlist(strsplit(cln,">")),collapse=">")
cln <-paste(unlist(strsplit(cln,"'")),collapse="'")
return(cln)
}
makevectorxml<-function(code,objt,name=""){
xmlcode<-code
if(name==""){
varname<-cleanNames(deparse(substitute(obj)))
}else{
varname<-name
}
obj<-objt
n <- 0; m <- 0
mydim <- dim(obj)
if(!is.null(mydim)){
n <- mydim[1]; m <- mydim[2]
}else{
n <- length(obj); m <- 1
}
if(is.matrix(obj)) obj<-as.vector(obj)
if(typeof(obj)=="language") obj<-toString(obj)
if(typeof(obj)=="logical") obj<-as.character(obj)
if(class(obj)=="factor") obj<-as.vector(obj)
if(is.vector(obj) && is.numeric(obj)){
xmlcode<-paste(xmlcode,"<variable name=\"",varname,"\" type=\"numeric\" n=\"", n, "\" m=\"", m, "\">",sep="")
s <- sapply(X=obj, function(str){
return(
paste("<v>",iconv(replaceXMLchars(toString(str)), to="UTF-8"),"</v>",sep="")
)})
xmlcode<-paste(xmlcode,paste(s, collapse=""),"</variable>\n")
}
if(is.vector(obj) && is.character(obj)){
xmlcode<-paste(xmlcode,"<variable name=\"",varname,"\" type=\"character\">\n",sep="")
s <- sapply(X=obj, function(str){
return(
paste("<v>",iconv(replaceXMLchars(toString(str)), to="UTF-8"),"</v>",sep="")
)})
xmlcode<-paste(xmlcode,paste(s, collapse=""),"</variable>\n")
}
return(xmlcode)
}
makexml<-function(obj,name=""){
xmlcode<-"<?xml version=\"1.0\"?>\n<root>\n"
if(!is.list(obj)){
xmlcode<-makevectorxml(xmlcode,obj,cleanNames(name))
}else{
objnames<-names(obj)
for (i in 1:length(obj)){
xmlcode<-makevectorxml(xmlcode,obj[[i]],cleanNames(objnames[[i]]))
}
}
xmlcode<-paste(xmlcode,"</root>\n",sep="")
return(xmlcode)
}
PERSON_ID<-c(166532, 166551, 166640, 166651, 166668, 166705, 166736, 166745, 166806, 166822);
OUTCOME<-c(1, 1, 1, 1, 1, 0, 0, 0, 0, 0);
tnb<-c(48.0, 48.0, 49.0, 48.0, 48.0, 49.0, 48.0, 48.0, 49.0, 48.0);
gxy<-c(48.0, 48.0, 49.0, 49.0, 48.0, 49.0, 49.0, 48.0, 49.0, 48.0);
AGE1<-c(76.0, 81.0, 74.0, 72.0, 73.0, 73.0, 81.0, 74.0, 74.0, 85.0);
matrix <- cbind(PERSON_ID,OUTCOME,tnb,gxy,AGE1)
df <- as.data.frame(matrix)
library(MatchIt)
fm <- matchit(OUTCOME ~ tnb + gxy + AGE1, data = df, method = "nearest", replace = TRUE, ratio = 1)
result <- summary(fm)
sum <- result$sum.all
sa_0_distance <- unlist(sum[1, 1:7], use.names=FALSE)
sa_1_tnb <- unlist(sum[2, 1:7], use.names=FALSE)
sa_2_gxy <- unlist(sum[3, 1:7], use.names=FALSE)
sa_3_AGE1 <- unlist(sum[4, 1:7], use.names=FALSE)
mat <- result$sum.matched
mat_0_distance <- unlist(mat[1, 1:7], use.names=FALSE)
mat_1_tnb <- unlist(mat[2, 1:7], use.names=FALSE)
mat_2_gxy <- unlist(mat[3, 1:7], use.names=FALSE)
mat_3_AGE1 <- unlist(mat[4, 1:7], use.names=FALSE)
red <- result$reduction
red_0_distance <- unlist(red[1, 1:4], use.names=FALSE)
red_1_tnb <- unlist(red[2, 1:4], use.names=FALSE)
red_2_gxy <- unlist(red[3, 1:4], use.names=FALSE)
red_3_AGE1 <- unlist(red[4, 1:4], use.names=FALSE)
ss <- result$nn
mData <- unlist(match.data(fm)[1], use.names=FALSE)
out <- list(sa_distance = sa_0_distance, mat_distance = mat_0_distance, red_distance = red_0_distance, sa_tnb = sa_1_tnb, mat_tnb = mat_1_tnb, red_tnb = red_1_tnb, sa_gxy = sa_2_gxy, mat_gxy = mat_2_gxy, red_gxy = red_2_gxy, sa_AGE1 = sa_3_AGE1, mat_AGE1 = mat_3_AGE1, red_AGE1 = red_3_AGE1, size = ss, ids = mData)
cat(makexml(obj=out, name="out"), file="C:/Users/Lenovo/AppData/Local/Temp/ROutput8334329596424358515")
为了方便显示,对每个变量我只截取了十个元素。从上面可以看到,我干了四件事:
1. 传入的数据必须根据实际情况转型成需要的类型,比如这里所有的变量值都是数字
2. 将每个变量的值数组直接传入 R 的数组里,然后使用 as.data.frame 转成 data.frame, 这样就省去了些 CSV 文件的麻烦,这个在之前的一个文章里提到了
3. 将需要返回的复杂类型(比如 list)转成 vector,使用 unlist 函数
4. 所有放入最终返回类型的 out 里面的元素都必须有一个名字
里面的样子:

获取各个 Matrix 的函数:

我的程序是这样的:
RCaller caller = initRCaller(new RCallerTemplate() {
@Override
public void addRCode(RCode code) {
code.addRCode("df <- read.csv('C:/Users/Lenovo/Desktop/ccc.csv', header=TRUE)");
code.addRCode("library(MatchIt)");
code.addRCode("fm <- matchit(censor ~ covariate1 + covariate2, method='nearest', data=df)");
code.addRCode("result <- summary(fm)");
code.addRCode("sa <- result$sum.all");
code.addRCode("mat <- result$sum.matched");
code.addRCode("red <- result$reduction");
code.addRCode("ss <- result$nn");
code.addRCode("mData <- match.data(fm)");
code.addRCode("out <- list(sum, mat, red, ss, mData)");
}
});
caller.runAndReturnResult("out");
double[] result = caller.getParser().getAsDoubleArray("out");程序运行时,RCaller 报 Rcaller Error in strsplit(names, "\\.") 错误,逐行注释调试,如果直接获取 sa , 报
com.github.rcaller.exception.ParseException: Variable sa not found但是获取 ss 是没有问题的,能正确取得值,只能进入 RCaller 里面调试源码了。大致得出下面 3点:
1. RCaller 把R代码写入文件中,调用Rscript执行;
2. 执行之后RCaller通过试图把R结果转成xml格式,返回给Java;我们的R代码没有问题,问题出在转xml的部分;
3. RCaller转xml的时候,它默认每个数据(包括list),每一列都要有名字,而我们java代码里边的out变量,没有名字,所以objnames<-names(obj)为空,导致运行出错;
makexml<-function(obj,name=""){
xmlcode<-"<?xml version=\"1.0\"?>\n<root>\n"
if(!is.list(obj)){
print( cat( "not list:", name ) )
xmlcode<-makevectorxml(xmlcode,obj,name)
}else{
objnames<-names(obj)
for (i in 1:length(obj)){
print( cat( "not list:", objnames[[i]] ) )
xmlcode<-makevectorxml(xmlcode,obj[[i]],cleanNames(objnames[[i]]))
}
}
xmlcode<-paste(xmlcode,"</root>\n",sep="")
return(xmlcode)
}尝试着给每个列都取名字, 把Java代码写成这样:
output <- list( o1=sa, o2=mat, o3=red, o4=ss, o5=mData )
又会遇到 RCaller 的第二个问题,数据类型支持不全:
makevectorxml<-function(code,objt,name=""){
xmlcode<-code
if(name==""){
varname<-cleanNames(deparse(substitute(obj)))
}else{
varname<-name
}
obj<-objt
n <- 0; m <- 0
mydim <- dim(obj)
if(!is.null(mydim)){
n <- mydim[1]; m <- mydim[2]
}else{
n <- length(obj); m <- 1
}
if(is.matrix(obj)) obj<-as.vector(obj)
if(typeof(obj)=="language") obj<-toString(obj)
if(typeof(obj)=="logical") obj<-as.character(obj)
if(is.vector(obj) && is.numeric(obj)){
xmlcode<-paste(xmlcode,"<variable name=\"",varname,"\" type=\"numeric\" n=\"", n, "\" m=\"", m, "\">",sep="")
for (i in obj){
xmlcode<-paste(xmlcode,"<v>", toString(i), "</v>",sep="")
}
xmlcode<-paste(xmlcode,"</variable>\n",sep="")
}
if(is.vector(obj) && is.character(obj)){
xmlcode<-paste(xmlcode,"<variable name=\"",varname,"\" type=\"character\">\n",sep="")
for (i in obj){
xmlcode<-paste(xmlcode,"<v>",toString(i),"</v>",sep="")
}
xmlcode<-paste(xmlcode,"</variable>\n")
}
return(xmlcode)
}因为 sa, mat 的类型都是 list,而 ss 是其支持的类型,不然根本进入不了 if 语句里,原样返回了xmlcode而已,所以Java里只能看到ss,调用获取别的都出错。
> is.matrix( mat ) [1] FALSE > is.numeric( mat ) [1] FALSE > is.vector( mat ) [1] FALSE > is.character(mat) [1] FALSE > typeof(mat) [1] "list"
所以,对于复杂的类型返回,就不要使用 RCaller, 但是 RCaller 的 API 友好性真的不错,如果分析的结果比较简单,还是喜欢使用这个工具。
=================更新 @ 2017/09/26=====================
既然 RCaller 支持的类型比较有限,那么为了返回结果能够进入这些 if 语句块,我们是不是可以对结果数据进行转型,比如 mat 是一个 list 类型,我们是否有办法将其转型为 vector, 这样不就可以了。google 了下,发现了 Better way to convert list
to vector? 里面提到了 unlist(myList, use.names=FALSE)将转型和对 out 里面的每个返回值赋予一个名字,终于出结果了。但是发现了另外一个问题,具体描述见 difference between as.data.frame and read.csv in
R
其实,真正写程序的时候,是页面传变量的ID/Name, 后台查询数据库得出值,因为不知道变量返回值的类型,我统一使用 String 接收,然后放入 RCaller 的 RCode里,生成 R 的完整程序里,可以看到每个变量的值都是字符串。把程序抓出来放到 RGui 里面,打印data.frame并不能看出其类型,但是可以通过 sapply 函数得知:
> sapply(df, class)
PERSON_ID OUTCOME tnb gxy AGE1
"factor" "factor" "factor" "factor" "factor"由于是 factor 类型,表示是离散值,非数字, matchit 不会把他们当数字处理,只罗列所有离散值。
解决办法有两个,一个就是在输入 RCode 之前,就将变量值转成数字型。另一个就是在 R 执行 matchit 之前,对 data.frame 的列进行转型:
newdf = transform( df, tnb = as.numeric( tnb ), AGE1=as.numeric( AGE1 ) )
sapply( newdf, class )
PERSON_ID OUTCOME tnb gxy AGE1
"factor" "factor" "numeric" "factor" "numeric"
最终,我采取了在传入 RCode 之前,就对数据转型成数字,然后传入 RCode。首先我的 R 程序的生成文件在 C:\Users\Lenovo\AppData\Local\Temp 路径下 (Lenovo是我的机器名),完整代码如下:
cleanNames<-function(names){
cln<-paste(unlist(strsplit(names,"\\.")),collapse="_")
cln<-paste(unlist(strsplit(cln,"<")),collapse="")
cln<-paste(unlist(strsplit(cln,">")),collapse="")
cln<-paste(unlist(strsplit(cln," ")),collapse="")
cln<-paste(unlist(strsplit(cln,"\\(")),collapse="")
cln<-paste(unlist(strsplit(cln,"\\)")),collapse="")
cln<-paste(unlist(strsplit(cln,"\\[")),collapse="")
cln<-paste(unlist(strsplit(cln,"\\]")),collapse="")
cln<-paste(unlist(strsplit(cln,"\\*")),collapse="")
cln<-paste(unlist(strsplit(cln,"&")),collapse="")
return(cln)
}
replaceXMLchars <- function(aStr){
cln <-paste(unlist(strsplit(aStr,"&")),collapse="&")
cln <-paste(unlist(strsplit(cln,"<")),collapse="<")
cln <-paste(unlist(strsplit(cln,">")),collapse=">")
cln <-paste(unlist(strsplit(cln,"'")),collapse="'")
return(cln)
}
makevectorxml<-function(code,objt,name=""){
xmlcode<-code
if(name==""){
varname<-cleanNames(deparse(substitute(obj)))
}else{
varname<-name
}
obj<-objt
n <- 0; m <- 0
mydim <- dim(obj)
if(!is.null(mydim)){
n <- mydim[1]; m <- mydim[2]
}else{
n <- length(obj); m <- 1
}
if(is.matrix(obj)) obj<-as.vector(obj)
if(typeof(obj)=="language") obj<-toString(obj)
if(typeof(obj)=="logical") obj<-as.character(obj)
if(class(obj)=="factor") obj<-as.vector(obj)
if(is.vector(obj) && is.numeric(obj)){
xmlcode<-paste(xmlcode,"<variable name=\"",varname,"\" type=\"numeric\" n=\"", n, "\" m=\"", m, "\">",sep="")
s <- sapply(X=obj, function(str){
return(
paste("<v>",iconv(replaceXMLchars(toString(str)), to="UTF-8"),"</v>",sep="")
)})
xmlcode<-paste(xmlcode,paste(s, collapse=""),"</variable>\n")
}
if(is.vector(obj) && is.character(obj)){
xmlcode<-paste(xmlcode,"<variable name=\"",varname,"\" type=\"character\">\n",sep="")
s <- sapply(X=obj, function(str){
return(
paste("<v>",iconv(replaceXMLchars(toString(str)), to="UTF-8"),"</v>",sep="")
)})
xmlcode<-paste(xmlcode,paste(s, collapse=""),"</variable>\n")
}
return(xmlcode)
}
makexml<-function(obj,name=""){
xmlcode<-"<?xml version=\"1.0\"?>\n<root>\n"
if(!is.list(obj)){
xmlcode<-makevectorxml(xmlcode,obj,cleanNames(name))
}else{
objnames<-names(obj)
for (i in 1:length(obj)){
xmlcode<-makevectorxml(xmlcode,obj[[i]],cleanNames(objnames[[i]]))
}
}
xmlcode<-paste(xmlcode,"</root>\n",sep="")
return(xmlcode)
}
PERSON_ID<-c(166532, 166551, 166640, 166651, 166668, 166705, 166736, 166745, 166806, 166822);
OUTCOME<-c(1, 1, 1, 1, 1, 0, 0, 0, 0, 0);
tnb<-c(48.0, 48.0, 49.0, 48.0, 48.0, 49.0, 48.0, 48.0, 49.0, 48.0);
gxy<-c(48.0, 48.0, 49.0, 49.0, 48.0, 49.0, 49.0, 48.0, 49.0, 48.0);
AGE1<-c(76.0, 81.0, 74.0, 72.0, 73.0, 73.0, 81.0, 74.0, 74.0, 85.0);
matrix <- cbind(PERSON_ID,OUTCOME,tnb,gxy,AGE1)
df <- as.data.frame(matrix)
library(MatchIt)
fm <- matchit(OUTCOME ~ tnb + gxy + AGE1, data = df, method = "nearest", replace = TRUE, ratio = 1)
result <- summary(fm)
sum <- result$sum.all
sa_0_distance <- unlist(sum[1, 1:7], use.names=FALSE)
sa_1_tnb <- unlist(sum[2, 1:7], use.names=FALSE)
sa_2_gxy <- unlist(sum[3, 1:7], use.names=FALSE)
sa_3_AGE1 <- unlist(sum[4, 1:7], use.names=FALSE)
mat <- result$sum.matched
mat_0_distance <- unlist(mat[1, 1:7], use.names=FALSE)
mat_1_tnb <- unlist(mat[2, 1:7], use.names=FALSE)
mat_2_gxy <- unlist(mat[3, 1:7], use.names=FALSE)
mat_3_AGE1 <- unlist(mat[4, 1:7], use.names=FALSE)
red <- result$reduction
red_0_distance <- unlist(red[1, 1:4], use.names=FALSE)
red_1_tnb <- unlist(red[2, 1:4], use.names=FALSE)
red_2_gxy <- unlist(red[3, 1:4], use.names=FALSE)
red_3_AGE1 <- unlist(red[4, 1:4], use.names=FALSE)
ss <- result$nn
mData <- unlist(match.data(fm)[1], use.names=FALSE)
out <- list(sa_distance = sa_0_distance, mat_distance = mat_0_distance, red_distance = red_0_distance, sa_tnb = sa_1_tnb, mat_tnb = mat_1_tnb, red_tnb = red_1_tnb, sa_gxy = sa_2_gxy, mat_gxy = mat_2_gxy, red_gxy = red_2_gxy, sa_AGE1 = sa_3_AGE1, mat_AGE1 = mat_3_AGE1, red_AGE1 = red_3_AGE1, size = ss, ids = mData)
cat(makexml(obj=out, name="out"), file="C:/Users/Lenovo/AppData/Local/Temp/ROutput8334329596424358515")
为了方便显示,对每个变量我只截取了十个元素。从上面可以看到,我干了四件事:
1. 传入的数据必须根据实际情况转型成需要的类型,比如这里所有的变量值都是数字
2. 将每个变量的值数组直接传入 R 的数组里,然后使用 as.data.frame 转成 data.frame, 这样就省去了些 CSV 文件的麻烦,这个在之前的一个文章里提到了
3. 将需要返回的复杂类型(比如 list)转成 vector,使用 unlist 函数
4. 所有放入最终返回类型的 out 里面的元素都必须有一个名字
相关文章推荐
- Spring MVC使用@ResponseBody返回JSON数据406以及乱码问题解决方案
- Spring MVC使用@ResponseBody返回JSON数据406以及乱码问题解决方案
- ajaxfileupload以JSON为返回数据类型出现的因符号无法解析的错误的解决方案
- ajaxfileupload以JSON为返回数据类型出现的因符号无法解析的错误的解决方案
- 关于mysql无法添加中文数据的问题以及解决方案
- WebAPI返回数据类型解惑 以及怎样解决Extjs无法解析返回的xml
- 在基于Mybatis持久层框架,使用数据库事务时,插入一条数据后,无法返回主键ID的问题研究
- WebAPI返回数据类型解惑 以及怎样解决Extjs无法解析返回的xml
- Spring MVC使用@ResponseBody返回JSON数据406以及乱码问题解决方案
- WebAPI返回数据类型解惑 以及怎样解决Extjs无法解析返回的xml
- 由JDBC事务引起的锁状态以及内存数据无法写入数据库的问题
- ie浏览器 spring mvc返回json数据弹出下载页面 解决方案
- spring boot最新教程(四):返回json数据以及集成fastjson的使用
- Android的okhttp的post请求,php返回json数据。以及遇到的okhttp dispatcher问题,和json解析遇到的问题
- 一个SDE无法启动的问题以及解决方案
- ajaxFileUpload插件,C#返回Json数据报错问题的解决方案
- WebRTC音视频引擎研究(2)--VoiceEngine音频编解码器数据结构以及参数设置
- 新浪微博SDK授权后无法返回应用解决方案
- Visual C++ 6.0如何配置文件以及无法使用配置文件(Profile)的解决方案
- HTTP接口不同项目网页之间数据交互跨域以及打开的窗口无法跳出关掉的问题
